Servicios Personalizados
Revista
Articulo
Indicadores
-
 Citado por SciELO
Citado por SciELO
Links relacionados
-
 Similares en
SciELO
Similares en
SciELO  uBio
uBio
Compartir
Revista argentina de microbiología
versión impresa ISSN 0325-7541versión On-line ISSN 1851-7617
Rev. argent. microbiol. v.39 n.1 Ciudad Autónoma de Buenos Aires ene./mar. 2007
Detección de variabilidad genética en aislamientos de Cercospora kikuchii contaminantes de un mismo sembradío de soja
M. C. Lurá*, J. A. Di Conza, A. M. González, M. G. Latorre Rapela, L. Turino, M. M. Ibáñez, V. Iacona
Cátedra de Microbiología General, Facultad de Bioquímica y Ciencias Biológicas, Universidad Nacional del Litoral, Ciudad Universitaria, Paraje El Pozo (3000) Santa Fe, Argentina.
*Correspondencia. E-mail: mclura@fbcb.unl.edu.ar; eocalafell@ciudad.com.ar
RESUMEN
El conocimiento de la epidemiología y la estructura poblacional de Cercospora kikuchii está poco desarrollado y no se han comunicado estudios al respecto en la Argentina. El objetivo de este trabajo fue seleccionar oligonucleótidos que permitan detectar variabilidad genética en aislamientos de C. kikuchii obtenidos a partir de soja proveniente de un mismo sembradío, mediante la aplicación de RAPD. Se trabajó con 6 aislamientos de C. kikuchii, 5 de ellos se obtuvieron a partir de trozos de tejido enfermo y el restante provenía de una colección de cultivos. De los 7 oligonucleótidos empleados, 5 resultaron útiles para el estudio poblacional de los aislamientos de C. kikuchii.
Palabras clave: Cercospora kikuchii, RAPD, variabilidad genética
ABSTRACT
Detection of genetic variability in Cercospora kikuchii isolates from a single soybean field. Current knowledge about epidemiology and population structure of Cercospora kikuchii is little developed and no studies regarding this subject have been reported in Argentina. The aim of this work was to select primers to study genetic variability in C. kikuchii isolated from the same soybean field using RAPD (Random Amplified Polymorphism DNA). RAPD was applied to the DNA of 5 C. kikuchii, isolated from diseased tissue of the soybean in the same field, another isolate, from a strain collection. Out of seven primers, five of them proved to be useful to study the population of C. kikuchii isolates.
Key words: Cercospora kikuchii, RAPD, genetic variability
La soja (Glycine max L. Merr.) constituye el principal producto de la agricultura argentina. Las denominadas "enfermedades de final de ciclo" son algunas de las que más frecuentemente afectan estos cultivos, entre ellas, el tizón de la hoja y la mancha púrpura de la semilla, provocadas ambas por Cercospora kikuchii (T. Matsumoto & Tomoyasu).
Este fitopatógeno tiene una amplia distribución mundial (1) y es uno de los hongos prevalentes en los cultivos de soja en la provincia de Santa Fe. A pesar de que diferentes autores coinciden en que el conocimiento de su estructura poblacional es de suma importancia para la prevención y control de las enfermedades que provoca (1, 10), hasta la fecha no se han comunicado estudios moleculares de la población de C. kikuchii en Argentina.
En su tesis doctoral, Cai (1) logró detectar diversidad en los aislamientos de C. kikuchii que infectaban la soja de distintos lugares de EE.UU. Para ello empleó diferentes técnicas moleculares, entre ellas RAPD.
El RAPD (Random Amplified Polymorphysm DNA) es un método de PCR (14) rápido y sencillo que genera un patrón de "huellas digitales", lo que contribuye a la tipificación con fines epidemiológicos. Esta técnica presenta un alto poder de resolución y, según el oligo-nucleótido que se utiliza, permite caracterizar una determinada especie o detectar diferentes genotipos en aislamientos estrechamente relacionados, lo que contribuye al mejor entendimiento de las diferencias genéticas entre las especies fúngicas patógenas de plantas (3, 8). Su mayor inconveniente es la baja reproducibilidad entre los diferentes laboratorios, lo que hace necesario poner a punto la técnica en cada ámbito donde se realiza (4, 7, 9).
El objetivo de este trabajo fue seleccionar oligonucleótidos que permitan detectar la variabilidad genética en aislamientos de Cercospora kikuchii obtenidos a partir de soja proveniente de un mismo sembradío, mediante la aplicación de RAPD.
Se trabajó con 5 aislamientos de C. kikuchii, obtenidos a partir de la soja cultivada en un campo de la localidad de San Jerónimo Norte, ubicado a aproximadamente 45 km de la ciudad de Santa Fe, y con una cepa de la colección NITE Biological Resource Center (NBRC): Cercospora kikuchii NBRC 6711.
Para el aislamiento de los hongos regionales se seleccionaron las plantas (estado fenológico R6) con síntomas visibles de tizón de la hoja, las que se extrajeron con raíz y se remitieron al laboratorio. Los hongos se aislaron colocando trozos de tejido enfermo en cámara húmeda a fin de estimular su esporulación, según la técnica descrita por Salvador et al. (11). Verificado el crecimiento de las estructuras conidiales, éstas fueron repicadas sobre agar papa dextrosa (PDA). Los cultivos se incubaron a 26 ± 0,5 °C y se sometieron a un régimen de iluminación (luz fría) con fotoperíodos de 12 h. Los aislamientos obtenidos se denominaron CKCO, CKCB, CKCC, CKCD, CKCH. La caracterización fenotípica se llevó a cabo utilizando los criterios taxonómicos clásicos y fisiológicos, incluyendo la producción de cercosporina (2, 5).
El ADN de cada hongo aislado se extrajo según Lee y Taylor (6). Los RAPDs se efectuaron según Williams et al. (14). Se utilizaron 7 oligonucleótidos (FAGOS/Ruralex, Argentina): OPA-01 (5'-CAGGCCCTTC-3'), OPA-03 (5'-AGTCAGCCAC-3'), OPA-05 (5'-AGGGGTCTTG-3'), OPA-08 (5'-GTGACGTAGG-3'), OPH-18 (5'-GAATC GGCCA-3'), y dos oligonucleótidos pertenecientes al RAPD Primer Set #1 (University of British Columbia): 5 (5'-CCTGGGTTCC-3') y 8 (5'-CCTGGCGGTA-3´), denominados MC5 y MC8, respectivamente.
La reacción de RAPD se efectuó con un volumen total de 50 µl que contenía: 2,5 mM MgCl2, 125 µM de cada uno de los dNTPs (InbioWay), 1 µM de oligonucleótido, 5 U de Taq DNA polimerasa (InbioWay) y 20 ng de ADN por reacción.
La amplificación se realizó en un MJ Research Thermal Cycler programado para 1 ciclo de 5min a 95 °C, 40 ciclos de 75s a 94 °C, 90s a 36 °C y 150s a 72 °C y 1 ciclo final de 10min a 72 °C.
Los productos de amplificación se analizaron por electroforesis en geles de agarosa 1,5% con 1x TBE (0,089 M Tris-borato, 0,002 M EDTA) y fueron teñidos con bromuro de etidio (12). Como marcadores de masa molecular se utilizaron Lambda Hind III/EcoRI (Promega) y 100-bp DNA ladder (Promega).
La ausencia o presencia de bandas polimórficas se consideró como 0 ó 1, respectivamente, y a cada una se la trató como carácter independiente, más allá de la intensidad de su fluorescencia. Para determinar la similitud entre los hongos, se obtuvo la matriz de distancia mediante el programa informático RAPDistance 1.04, aplicando el algoritmo de Dice (D). La relación entre los diferentes aislamientos estudiados se representó gráficamente mediante un dendrograma, utilizando el método UPGMA (Unweighted Pair Group Method with Arithmetic Mean) del programa Molecular Evolutionary Genetic Analyses (MEGA).
En la Tabla 1 se resumen el número de fragmentos amplificados y los tamaños mínimos y máximos entre los cuales estuvieron comprendidos. El patrón de bandas generado en cada caso y el polimorfismo observado fueron muy reproducibles.
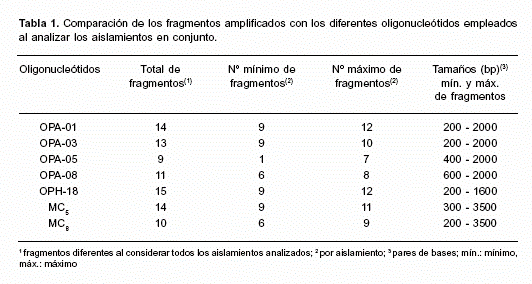
Todos aquellos aislamientos que presentaron perfiles idénticos con un mismo oligonucleótido fueron reunidos en un grupo.
El hallazgo de valores de disimilitud bajos (Figura 1) indicó una estrecha relación entre los aislamientos analizados. A pesar de ello, pudieron diferenciarse entre 3 y 4 grupos con la mayoría de los oligonucleótidos (Tabla 2), los que fueron designados I, II, III y IV. La cepa de colección CK6711, utilizada como control no relacionado, presentó un polimorfismo distinto del que mostraron los aislamientos regionales con todos los oligonucleótidos ensayados, a excepción de MC8, lo que se atribuyó a que dicho hongo no está relacionado epidemiológicamente con el resto.


Es importante destacar que los aislamientos que conformaron un grupo a partir del análisis con un determinado oligonucleótido, también se mantuvieron agrupados cuando el análisis se efectuó con otro oligonucleótido. Como se observa en la Tabla 2, los hongos regionales CKCB, CKCC y CKCH constituyeron un grupo en todos los ensayos, excepto cuando se empleó MC8. Curiosamente CKCO, en general, no pudo agruparse con los anteriormente señalados, lo que pone en evidencia la existencia de mayores diferencias en su genoma. Por su parte, CKCD mostró un patrón irregular de agrupación. Esta distribución se encuentra representada gráficamente en la Figura 1, en la que se visualizan dos de los dendrogramas obtenidos. De manera similar a lo reportado en este informe, Wang et al. lograron demostrar, mediante RAPD, la existencia de distintos grupos de C. zeaemaydis que enfermaban al maíz cultivado en un mismo campo (13).
En su tesis, Cai (1) indica haber trabajado con 12 oligonucleótidos pertenecientes a la serie OPA (OPA-01-OPA-12) y señala que OPA-05 y OPA-08 fueron los oligonucleótidos que le proporcionaron la mayor evidencia de variación entre los aislamientos estudiados. En este trabajo, OPA-03 y OPA-05 permitieron ordenar los hongos en 4 grupos. Sin embargo, con OPA-05 el número de bandas observado para algunos aislamientos fue bajo, lo que representa una desventaja en su utilización con fines epidemiológicos para los aislamientos de la zona. Por el contrario, MC8 generó un número apreciable de productos de PCR, aunque sólo permitió distinguir 2 grupos (Tabla 2), sin diferenciar la cepa utilizada como control no relacionado, de lo que podría inferirse que dicho oligonucleótido tiene un bajo poder de discriminación.
Sobre la base de las consideraciones anteriormente expuestas, se concluyó que fue posible detectar polimorfismo en el genoma de C. kikuchii proveniente de un mismo sembradío de soja mediante la aplicación de la técnica de RAPD, y que los oligonucleótidos OPA-01, OPA-03, OPA-08, OPH-18 y MC5 resultaron útiles para el estudio de diversidad genética entre distintos aislamientos.
Los resultados obtenidos en este trabajo constituyen un aporte a la comunidad agrícola, ya que brindan información que permite profundizar aspectos epidemiológicos sobre el patógeno responsable de una de las enfermedades más relevantes de fin de ciclo de la soja cultivada en la región.
Agradecimientos: el presente trabajo se realizó en el marco del Proyecto PICTO 08-13208, financiado por ANPCYT. Los autores desean agradecer a los Ing. Agrónomos Margarita Sillón y Eugenio Astegiano por la donación de las plantas de soja y a la Dra. Rosana Massa por la revisión desinteresada y valiosa del manuscrito.
Bibliografía
1. Cai G. Population structure of Cercospora kikuchii, the causal agent of Cercospora Leaf Blight and Purple Seed Stain in soybean, as revealed by random amplified polymorphic DNA and microsatellite-primed PCR. En: Cai G. Cercospora Leaf Blight of soybean: pathogen vegetative compatibility groups, population structure, and host resistance. Louisiana University, Doctoral Thesis, 2003, p. 34-57. Disponible en: http://etd.lsu.edu/docs/available/etd-12112003-143624/ [ Links ]
2. Daub ME. Cercosporin, a photosensitizing toxin from Cercospora species. Phytopathology 1982; 72: 370-4. [ Links ]
3. Drenth A, Irwin JAG. Routine DNA based diagnostic tests for Phytophthora. Rural Industries Research and Development Corporation. Kingston, Australia, 2001. Disponible en: www.rirdc.gov.au/reports/Index.htm. [ Links ]
4. He Q, Viljanen MK, Mertsola J. Effects of thermocyclers and primers on the reproducibility of banding patterns in randomly amplified polymorphic DNA analysis. Mol Cell Probes 1994; 8: 155-9. [ Links ]
5. Jenns AE, Daub ME, Upchurch R. Regulation of cercosporin accumulation in culture by medium and temperature manipulation. Phytopathology 1989; 79: 213-9. [ Links ]
6. Lee SI, Taylor JW. Isolation DNA from fungal mycelia and single spores. En: Innis MA, Gelfand DH, Sninsky JJ, Write TJ, editors. PCR protocols. A guide to methods and applications. San Diego, Academic Press, 1990, p. 282-6. [ Links ]
7. MacPherson JM, Eckstein PE, Scoles GJ, Gajadhar AA. Variability of the random amplified polymorphic DNA assay among thermal cyclers, and effects of primer and DNA concentration. Mol Cell Probes 1993; 7: 293-9. [ Links ]
8. Martínez Culebras PV. Caracterización y diagnóstico molecular de las cepas de Colletotrichum patógenas en plantas de fresa. Valencia, Universitat de València, Tesis Doctoral, 1999. [ Links ]
9. Meunier JR, Grimont PA. Factors affecting reproducibility of random amplified polymorphic DNA fingerprinting. Res Microbiol 1993; 144: 373-9. [ Links ]
10. Orth CE, Schuh W. Resistance of 17 soybean cultivars to foliar, latent, and seed infection by Cercospora kikuchii. Plant Dis 1994; 78: 661-4. [ Links ]
11. Salvador D, Garrido M. Características culturales y patogenicidad del hongo causante de la mancha en cadena del sorgo. Fitopatol Venez 1990; 3: 11-5. [ Links ]
12. Sambrook J, Fritsch EF, Maniatis T. Molecular cloning: a laboratory manual. New York, Cold Spring Harbor, Laboratory Press, 1989. [ Links ]
13. Wang J, Levy M, Dunkle LD. Sibling species of Cercospora associated with gray leaf spot of maize. Phytopathology 1998; 88: 1269-75. [ Links ]
14. Williams JGK, Kubelik AR, Livak KJ, Rafalski JA, Tingey SV. DNA polymorphisms amplified by arbitrary primers are useful as genetic markers. Nucleic Acids Res 1990; 18: 6531-5. [ Links ]
Recibido: 17/10/06
Aceptado: 11/12/06














